שיפור סיווג מאפיינים באמ�צעות גרעינים קוונטיים מוקרנים
הערכת שימוש: 80 דקות על מעבד Heron r3 (הערה: זוהי הערכה בלבד. זמן הריצה בפועל עשוי להשתנות.)
במדריך זה נדגים כיצד להריץ גרעין קוונטי מוקרן (PQK) עם Qiskit על מערך נתונים ביולוגי מהעולם האמיתי, בהתבסס על המאמר Enhanced Prediction of CAR T-Cell Cytotoxicity with Quantum-Kernel Methods [1].
PQK היא שיטה בלמידת מכונה קוונטית (QML) לקידוד נתונים קלאסיים למרחב מאפיינים קוונטי והקרנתם בחזרה לתחום הקלאסי, תוך שימוש במחשבים קוונטיים לשיפור בחירת המאפיינים. השיטה כוללת קידוד נתונים קלאסיים למצבים קוונטיים באמצעות Circuit קוונטי, בדרך כלל דרך תהליך הנקרא מיפוי מאפיינים, שבו הנתונים מומרים למרחב הילברט רב-ממדי. ה"הקרנה" מתייחסת לחילוץ מידע קלאסי מהמצבים הקוונטיים — על ידי מדידת אובסרבבלים ספציפיים — לשם בניית מטריצת גרעין שניתן להשתמש בה באלגוריתמים קלאסיים מבוססי גרעין כמו מכונות וקטור תמיכה. גישה זו מנצלת את היתרונות החישוביים של מערכות קוונטיות כדי להשיג ביצועים טובים יותר על משימות מסוימות בהשוואה לשיטות קלאסיות.
מדריך זה מניח גם היכרות כללית עם שיטות QML. לחקירה נו�ספת של QML, ראו בקורס Quantum machine learning ב-IBM Quantum Learning.
דרישות
לפני תחילת מדריך זה, ודאו שהתקנתם את הדברים הבאים:
- Qiskit SDK גרסה 2.0 ואילך, עם תמיכה בויזואליזציה
- Qiskit Runtime גרסה 0.40 ואילך (
pip install qiskit-ibm-runtime) - Category encoders 2.8.1 (
pip install category-encoders) - NumPy 2.3.2 (
pip install numpy) - Pandas 2.3.2 (
pip install pandas) - Scikit-learn 1.7.1 (
pip install scikit-learn) - Tqdm 4.67.1 (
pip install tqdm)
הגדרת סביבה
# Added by doQumentation — required packages for this notebook
!pip install -q category-encoders numpy pandas qiskit qiskit-ibm-runtime scipy scikit-learn tqdm
import warnings
# Standard libraries
import os
import numpy as np
import pandas as pd
# Machine learning and data processing
import category_encoders as ce
from scipy.linalg import inv, sqrtm
from sklearn.metrics.pairwise import rbf_kernel
from sklearn.model_selection import GridSearchCV, StratifiedKFold
from sklearn.svm import SVC
# Qiskit and Qiskit Runtime
from qiskit import QuantumCircuit
from qiskit.circuit import ParameterVector
from qiskit.circuit.library import UnitaryGate, ZZFeatureMap
from qiskit.quantum_info import SparsePauliOp, random_unitary
from qiskit.transpiler import generate_preset_pass_manager
from qiskit_ibm_runtime import (
Batch,
EstimatorOptions,
EstimatorV2 as Estimator,
QiskitRuntimeService,
)
# Progress bar
import tqdm
warnings.filterwarnings("ignore")
שלב 1: מיפוי קלטים קלאסיים לבעיה קוונטית
הכנת מערך הנתונים
במדריך זה אנחנו משתמשים במערך נתונים ביולוגי מהעולם האמיתי למשימת סיווג בינארי, שנוצר על ידי Daniels et al. (2022) וניתן להוריד מהחומר המשלים הכלול במאמר. הנתונים מורכבים מ-CAR T-cells — תאי T מהונדסים גנטית המשמשים באימונותרפיה לטיפול בסוגי סרטן מסוימים. תאי T, סוג של תאי חיסון, מוּשְׁנִים במעבדה כך שיבטאו קולטנים כימריים לאנטיגן (CARs) המכוונים לחלבונים ספציפיים על תאי הסרטן. תאי T מוּשְׁנִים אלה מסוגלים לזהות ולהשמיד תאי סרטן ביעילות רבה יותר. מאפייני הנתונים הם המוטיפים של CAR T-cells, המתייחסים לרכיב המבני או הפונקציונלי הספציפי של ה-CAR המהונדס לתוך תאי ה-T. בהתבסס על מוטיפים אלו, משימתנו היא לחזות את הציטוטוקסיות של CAR T-cell נתון — לסווגו כרעיל או לא-רעיל. להלן פונקציות העזר לעיבוד מקדים של מערך נתונים זה.
def preprocess_data(dir_root, args):
"""
Preprocess the training and test data.
"""
# Read from the csv files
train_data = pd.read_csv(
os.path.join(dir_root, args["file_train_data"]),
encoding="unicode_escape",
sep=",",
)
test_data = pd.read_csv(
os.path.join(dir_root, args["file_test_data"]),
encoding="unicode_escape",
sep=",",
)
# Fix the last motif ID
train_data[train_data == 17] = 14
train_data.columns = [
"Cell Number",
"motif",
"motif.1",
"motif.2",
"motif.3",
"motif.4",
"Nalm 6 Cytotoxicity",
]
test_data[test_data == 17] = 14
test_data.columns = [
"Cell Number",
"motif",
"motif.1",
"motif.2",
"motif.3",
"motif.4",
"Nalm 6 Cytotoxicity",
]
# Adjust motif at the third position
if args["filter_for_spacer_motif_third_position"]:
train_data = train_data[
(train_data["motif.2"] == 14) | (train_data["motif.2"] == 0)
]
test_data = test_data[
(test_data["motif.2"] == 14) | (test_data["motif.2"] == 0)
]
train_data = train_data[
args["motifs_to_use"] + [args["label_name"], "Cell Number"]
]
test_data = test_data[
args["motifs_to_use"] + [args["label_name"], "Cell Number"]
]
# Adjust motif at the last position
if not args["allow_spacer_motif_last_position"]:
last_motif = args["motifs_to_use"][len(args["motifs_to_use"]) - 1]
train_data = train_data[
(train_data[last_motif] != 14) & (train_data[last_motif] != 0)
]
test_data = test_data[
(test_data[last_motif] != 14) & (test_data[last_motif] != 0)
]
# Get the labels
train_labels = np.array(train_data[args["label_name"]])
test_labels = np.array(test_data[args["label_name"]])
# For the classification task use the threshold to binarize labels
train_labels[train_labels > args["label_binarization_threshold"]] = 1
train_labels[train_labels < 1] = args["min_label_value"]
test_labels[test_labels > args["label_binarization_threshold"]] = 1
test_labels[test_labels < 1] = args["min_label_value"]
# Reduce data to just the motifs of interest
train_data = train_data[args["motifs_to_use"]]
test_data = test_data[args["motifs_to_use"]]
# Get the class and motif counts
min_class = np.min(np.unique(np.concatenate([train_data, test_data])))
max_class = np.max(np.unique(np.concatenate([train_data, test_data])))
num_class = max_class - min_class + 1
num_motifs = len(args["motifs_to_use"])
print(str(max_class) + ":" + str(min_class) + ":" + str(num_class))
train_data = train_data - min_class
test_data = test_data - min_class
return (
train_data,
test_data,
train_labels,
test_labels,
num_class,
num_motifs,
)
def data_encoder(args, train_data, test_data, num_class, num_motifs):
"""
Use one-hot or binary encoding for classical data representation.
"""
if args["encoder"] == "one-hot":
# Transform to one-hot encoding
train_data = np.eye(num_class)[train_data]
test_data = np.eye(num_class)[test_data]
train_data = train_data.reshape(
train_data.shape[0], train_data.shape[1] * train_data.shape[2]
)
test_data = test_data.reshape(
test_data.shape[0], test_data.shape[1] * test_data.shape[2]
)
elif args["encoder"] == "binary":
# Transform to binary encoding
encoder = ce.BinaryEncoder()
base_array = np.unique(np.concatenate([train_data, test_data]))
base = pd.DataFrame(base_array).astype("category")
base.columns = ["motif"]
for motif_name in args["motifs_to_use"][1:]:
base[motif_name] = base.loc[:, "motif"]
encoder.fit(base)
train_data = encoder.transform(train_data.astype("category"))
test_data = encoder.transform(test_data.astype("category"))
train_data = np.reshape(
train_data.values, (train_data.shape[0], num_motifs, -1)
)
test_data = np.reshape(
test_data.values, (test_data.shape[0], num_motifs, -1)
)
train_data = train_data.reshape(
train_data.shape[0], train_data.shape[1] * train_data.shape[2]
)
test_data = test_data.reshape(
test_data.shape[0], test_data.shape[1] * test_data.shape[2]
)
else:
raise ValueError("Invalid encoding type.")
return train_data, test_data
ניתן להריץ מדריך זה על ידי הרצת התא הבא, שיוצר אוטומטית את מבנה התיקיות הנדרש ומוריד את קובצי האימון והבדיקה ישירות לסביבה שלכם. אם כבר יש לכם קבצים אלה באופן מקומי, שלב זה ידרוס אותם בבטחה כדי להבטיח עקביות גרסאות.
## Download dataset
# Create data directory if it doesn't exist
!mkdir -p data_tutorial/pqk
# Download the training and test sets from the official Qiskit documentation repo
!wget -q --show-progress -O data_tutorial/pqk/train_data.csv \
https://raw.githubusercontent.com/Qiskit/documentation/main/datasets/tutorials/pqk/train_data.csv
!wget -q --show-progress -O data_tutorial/pqk/test_data.csv \
https://raw.githubusercontent.com/Qiskit/documentation/main/datasets/tutorials/pqk/test_data.csv
!wget -q --show-progress -O data_tutorial/pqk/projections_train.csv \
https://raw.githubusercontent.com/Qiskit/documentation/main/datasets/tutorials/pqk/projections_train.csv
!wget -q --show-progress -O data_tutorial/pqk/projections_test.csv \
https://raw.githubusercontent.com/Qiskit/documentation/main/datasets/tutorials/pqk/projections_test.csv
# Check the files have been downloaded
!echo "Dataset files downloaded:"
!ls -lh data_tutorial/pqk/*.csv
args = {
"file_train_data": "train_data.csv",
"file_test_data": "test_data.csv",
"motifs_to_use": ["motif", "motif.1", "motif.2", "motif.3"],
"label_name": "Nalm 6 Cytotoxicity",
"label_binarization_threshold": 0.62,
"filter_for_spacer_motif_third_position": False,
"allow_spacer_motif_last_position": True,
"min_label_value": -1,
"encoder": "one-hot",
}
dir_root = "./"
# Preprocess data
train_data, test_data, train_labels, test_labels, num_class, num_motifs = (
preprocess_data(dir_root=dir_root, args=args)
)
# Encode the data
train_data, test_data = data_encoder(
args, train_data, test_data, num_class, num_motifs
)
14:0:15
אנחנו גם ממירים את מערך הנתונים כך ש- ייוצג כ- לצורכי קנה-מידה.
# Change 1 to pi/2
angle = np.pi / 2
tmp = pd.DataFrame(train_data).astype("float64")
tmp[tmp == 1] = angle
train_data = tmp.values
tmp = pd.DataFrame(test_data).astype("float64")
tmp[tmp == 1] = angle
test_data = tmp.values
אנחנו מאמתים את הגדלים והצורות של מערכי הנתונים לאימון ולבדיקה.
print(train_data.shape, train_labels.shape)
print(test_data.shape, test_labels.shape)
(172, 60) (172,)
(74, 60) (74,)
שלב 2: אופטימיזציה של הבעיה לביצוע על חומרה קוונטית
Circuit קוונטי
כעת נבנה את מפת המאפיינים שמטמיעה את מערך הנתונים הקלאסי שלנו במרחב מאפיינים רב-ממדי. לצורך הטמעה זו, אנחנו משתמשים ב-ZZFeatureMap מ-Qiskit.
feature_dimension = train_data.shape[1]
reps = 24
insert_barriers = True
entanglement = "pairwise"
# ZZFeatureMap with linear entanglement and a repetition of 2
embed = ZZFeatureMap(
feature_dimension=feature_dimension,
reps=reps,
entanglement=entanglement,
insert_barriers=insert_barriers,
name="ZZFeatureMap",
)
embed.decompose().draw(output="mpl", style="iqp", fold=-1)

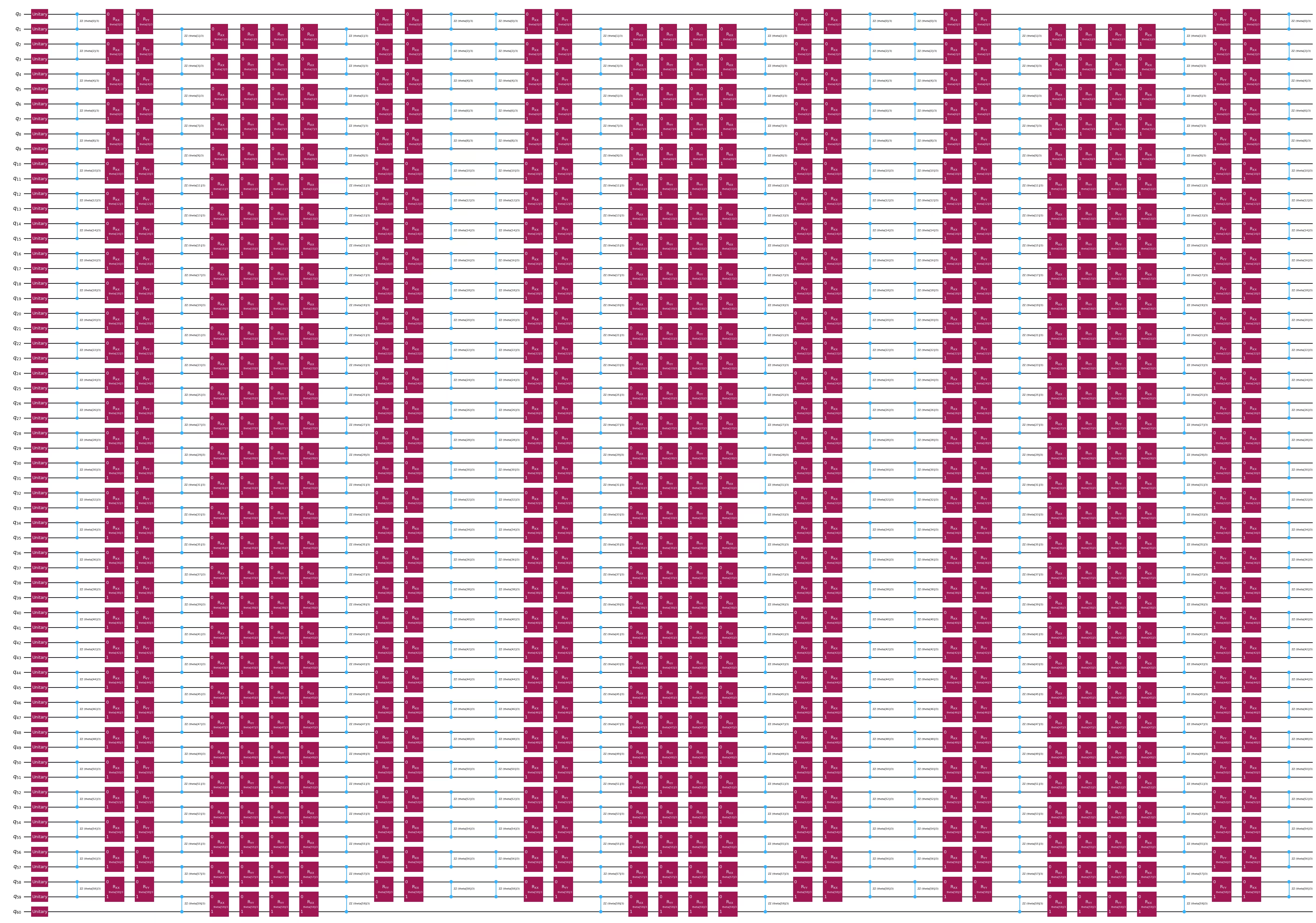
אפשרות הטמעה קוונטית נוספת היא אנזץ של אבולוציית האמילטוניאן חד-ממדי מסוג Heisenberg. ניתן לדלג על הרצת חלק זה אם ברצונכם להמשיך עם ה-ZZFeatureMap.
feature_dimension = train_data.shape[1]
num_qubits = feature_dimension + 1
embed2 = QuantumCircuit(num_qubits)
num_trotter_steps = 6
pv_length = feature_dimension * num_trotter_steps
pv = ParameterVector("theta", pv_length)
# Add Haar random single qubit unitary to each qubit as initial state
np.random.seed(42)
seeds_unitary = np.random.randint(0, 100, num_qubits)
for i in range(num_qubits):
rand_gate = UnitaryGate(random_unitary(2, seed=seeds_unitary[i]))
embed2.append(rand_gate, [i])
def trotter_circ(feature_dimension, num_trotter_steps):
num_qubits = feature_dimension + 1
circ = QuantumCircuit(num_qubits)
# Even
for i in range(0, feature_dimension, 2):
circ.rzz(2 * pv[i] / num_trotter_steps, i, i + 1)
for i in range(0, feature_dimension, 2):
circ.rxx(2 * pv[i] / num_trotter_steps, i, i + 1)
for i in range(0, feature_dimension, 2):
circ.ryy(2 * pv[i] / num_trotter_steps, i, i + 1)
# Odd
for i in range(1, feature_dimension, 2):
circ.rzz(2 * pv[i] / num_trotter_steps, i, i + 1)
for i in range(1, feature_dimension, 2):
circ.rxx(2 * pv[i] / num_trotter_steps, i, i + 1)
for i in range(1, feature_dimension, 2):
circ.ryy(2 * pv[i] / num_trotter_steps, i, i + 1)
return circ
# Hamiltonian evolution ansatz
for step in range(num_trotter_steps):
circ = trotter_circ(feature_dimension, num_trotter_steps)
if step % 2 == 0:
embed2 = embed2.compose(circ)
else:
reverse_circ = circ.reverse_ops()
embed2 = embed2.compose(reverse_circ)
embed2.draw(output="mpl", style="iqp", fold=-1)
שלב 3: ביצוע באמצעות פרימיטיבים של Qiskit
מדידת 1-RDMs
אבני הבניין המרכזיות של גרעיני קוונטום מוקרנים הן מטריצות הצפיפות המצומצמות (RDMs), המתקבלות דרך מדידות הקרנה של מפת המאפיינים הקוונטית. בשלב זה, נחשב את כל מטריצות הצפיפות המצומצמות לחד-קיוביט (1-RDMs), אשר יוזנו לאחר מכן אל פונקציית הגרעין האקספוננציאלי הקלאסית.
נבחן כיצד לחשב את ה-1-RDM עבור נקודת נתונים בודדת מהמסד לפני שנריץ על כלל הנתונים. ה-1-RDMs הן אוסף של מדידות חד-קיוביט של אופרטורי פאולי X, Y ו-Z על כל הקיוביטים. הסיבה לכך היא שניתן לבטא RDM חד-קיוביט באופן מלא כך:
תחילה, נבחר את ה-Backend שבו נשתמש.
service = QiskitRuntimeService()
backend = service.least_busy(
operational=True, simulator=False, min_num_qubits=133
)
target = backend.target
לאחר מכן נריץ את המעגל הקוונטי ונמדוד את ההקרנות. שימו לב שאנו מפעילים הפחתת שגיאות, כולל אקסטרפולציה של אפס רעש (ZNE).
# Let's select the ZZFeatureMap embedding for this example
qc = embed
num_qubits = feature_dimension
# Identity operator on all qubits
id = "I" * num_qubits
# Let's select the first training datapoint as an example
parameters = train_data[0]
# Bind parameter to the circuit and simplify it
qc_bound = qc.assign_parameters(parameters)
transpiler = generate_preset_pass_manager(
optimization_level=3, basis_gates=["u3", "cz"]
)
transpiled_circuit = transpiler.run(qc_bound)
# Transpile for hardware
transpiler = generate_preset_pass_manager(optimization_level=3, target=target)
transpiled_circuit = transpiler.run(transpiled_circuit)
# We group all commuting observables
# These groups are the Pauli X, Y and Z operators on individual qubits
observables_x = [
SparsePauliOp(id[:i] + "X" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_y = [
SparsePauliOp(id[:i] + "Y" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_z = [
SparsePauliOp(id[:i] + "Z" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
# We define the primitive unified blocs (PUBs) consisting of the embedding circuit,
# set of observables and the circuit parameters
pub_x = (transpiled_circuit, observables_x)
pub_y = (transpiled_circuit, observables_y)
pub_z = (transpiled_circuit, observables_z)
# Experiment options for error mitigation
num_randomizations = 300
shots_per_randomization = 100
noise_factors = [1, 3, 5]
experimental_opts = {}
experimental_opts["resilience"] = {
"measure_mitigation": True,
"zne_mitigation": True,
"zne": {
"noise_factors": noise_factors,
"amplifier": "gate_folding",
"extrapolated_noise_factors": [0] + noise_factors,
},
}
experimental_opts["twirling"] = {
"num_randomizations": num_randomizations,
"shots_per_randomization": shots_per_randomization,
"strategy": "active-accum",
}
# We define and run the estimator to obtain <X>, <Y> and <Z> on all qubits
estimator = Estimator(mode=backend, options=experimental_opts)
job = estimator.run([pub_x, pub_y, pub_z])
כעת נאחזר את התוצאות.
job_result_x = job.result()[0].data.evs
job_result_y = job.result()[1].data.evs
job_result_z = job.result()[2].data.evs
print(job_result_x)
print(job_result_y)
print(job_result_z)
[ 3.67865951e-03 1.01158571e-02 -3.95790878e-02 6.33984326e-03
1.86035759e-02 -2.91533268e-02 -1.06374793e-01 4.48873518e-18
4.70201764e-02 3.53997968e-02 2.53130819e-02 3.23903401e-02
6.06327843e-03 1.16313667e-02 -1.12387504e-02 -3.18457725e-02
-4.16445718e-04 -1.45609602e-03 -4.21737114e-01 2.83705669e-02
6.91332890e-03 -7.45363001e-02 -1.20139326e-02 -8.85566135e-02
-3.22648394e-02 -3.24228074e-02 6.20431299e-04 3.04225434e-03
5.72795792e-03 1.11288428e-02 1.50395861e-01 9.18380197e-02
1.02553163e-01 2.98312847e-02 -3.30298912e-01 -1.13979648e-01
4.49159340e-03 8.63861493e-02 3.05666566e-02 2.21463145e-04
1.45946735e-02 8.54537275e-03 -8.09805979e-02 -2.92608104e-02
-3.91243644e-02 -3.96632760e-02 -1.41187613e-01 -1.07363243e-01
1.81089440e-02 2.70778895e-02 1.45139414e-02 2.99480458e-02
4.99137134e-02 7.08789852e-02 4.30565759e-02 8.71287156e-02
1.04334798e-01 7.72191962e-02 7.10059720e-02 1.04650403e-01]
[-7.31765102e-05 7.42669174e-03 9.82277344e-03 5.92638249e-02
4.24120486e-02 -9.06473416e-03 4.55057675e-03 8.43494094e-03
6.92097339e-02 -6.82234424e-02 6.13509008e-02 3.94200491e-02
-1.24037979e-02 1.01976642e-01 7.90538600e-03 -7.19726160e-02
-1.19501703e-16 -1.03796614e-02 7.37382463e-02 1.97238568e-01
-3.59250635e-02 -2.67554009e-02 3.55010633e-02 7.68877990e-02
6.50677589e-05 -6.59298767e-03 -1.23719487e-02 -6.41938151e-02
1.95603072e-02 -2.48448551e-02 5.17784810e-02 -5.93767100e-02
3.11897681e-02 -3.91959720e-18 -4.47769148e-03 1.39202197e-01
-6.56387523e-02 -5.85665483e-02 9.52905894e-03 -8.61460731e-02
3.91790656e-02 -1.27544375e-01 1.63712244e-01 3.36816934e-04
2.26230028e-02 -2.45023393e-05 4.95635588e-03 1.44779564e-01
3.71625177e-02 3.65675948e-03 2.83694017e-02 -7.10500602e-02
-1.15467702e-01 6.21712129e-03 -4.80958959e-02 2.21021066e-02
7.99062499e-02 -1.87164076e-02 -3.67100369e-02 -2.38923731e-02]
[ 6.85871605e-01 5.07725024e-01 8.71024642e-03 3.34823455e-02
4.58684961e-02 9.44384189e-17 -4.46829296e-02 -2.91296778e-02
4.15466461e-02 2.89628330e-02 1.88624017e-03 5.37110446e-02
2.59579053e-03 1.39327071e-02 -2.90781778e-02 5.07209866e-03
5.83403000e-02 2.60764440e-02 4.45999706e-17 -6.66701417e-03
3.03215873e-01 2.26172533e-02 2.43105960e-02 4.98861041e-18
-2.45530791e-02 6.26940708e-02 1.21058073e-02 2.76675948e-04
2.63980996e-02 2.58302364e-02 7.47856723e-02 8.42728943e-02
5.70989097e-02 6.92955086e-02 -5.68313712e-03 1.32199452e-01
8.90511238e-02 -3.45204621e-02 -1.05445836e-01 6.03864150e-03
2.16291384e-02 8.22303162e-03 1.00856715e-02 6.28973151e-02
6.26727169e-02 6.15399206e-02 9.67320897e-02 1.03045269e-16
1.79688783e-01 -1.59960520e-02 -1.15422952e-02 9.60200470e-03
6.58396672e-02 7.78329830e-03 6.53226955e-02 2.45778685e-03
4.36694753e-03 5.75098762e-03 -2.48896201e-02 8.33740755e-05]
נדפיס את גודל המעגל ואת עומק השערים הדו-קיוביטיים.
print(f"qubits: {qc.num_qubits}")
print(
f"2q-depth: {transpiled_circuit.depth(lambda x: x.operation.num_qubits==2)}"
)
print(
f"2q-size: {transpiled_circuit.size(lambda x: x.operation.num_qubits==2)}"
)
print(f"Operator counts: {transpiled_circuit.count_ops()}")
transpiled_circuit.draw("mpl", fold=-1, style="clifford", idle_wires=False)
qubits: 60
2q-depth: 64
2q-size: 1888
Operator counts: OrderedDict({'rz': 6016, 'sx': 4576, 'cz': 1888, 'x': 896, 'barrier': 31})

כעת ניתן לעבור על כלל מסד הנתונים לאימון ולקבל את כל ה-1-RDMs.
אנחנו מספקים גם את תוצאות הניסוי שהרצנו על חומרה קוונטית. ניתן להריץ את האימון בעצמכם על ידי הגדרת הדגל שלהלן ל-True, או להשתמש בתוצאות ההקרנה שאנו מספקים.
# Set this to True if you want to run the training on hardware
run_experiment = False
# Identity operator on all qubits
id = "I" * num_qubits
# projections_train[i][j][k] will be the expectation value of the j-th Pauli operator (0: X, 1: Y, 2: Z)
# of datapoint i on qubit k
projections_train = []
jobs_train = []
# Experiment options for error mitigation
num_randomizations = 300
shots_per_randomization = 100
noise_factors = [1, 3, 5]
experimental_opts = {}
experimental_opts["resilience"] = {
"measure_mitigation": True,
"zne_mitigation": True,
"zne": {
"noise_factors": noise_factors,
"amplifier": "gate_folding",
"return_all_extrapolated": True,
"return_unextrapolated": True,
"extrapolated_noise_factors": [0] + noise_factors,
},
}
experimental_opts["twirling"] = {
"num_randomizations": num_randomizations,
"shots_per_randomization": shots_per_randomization,
"strategy": "active-accum",
}
options = EstimatorOptions(experimental=experimental_opts)
if run_experiment:
with Batch(backend=backend):
for i in tqdm.tqdm(
range(len(train_data)), desc="Training data progress"
):
# Get training sample
parameters = train_data[i]
# Bind parameter to the circuit and simplify it
qc_bound = qc.assign_parameters(parameters)
transpiler = generate_preset_pass_manager(
optimization_level=3, basis_gates=["u3", "cz"]
)
transpiled_circuit = transpiler.run(qc_bound)
# Transpile for hardware
transpiler = generate_preset_pass_manager(
optimization_level=3, target=target
)
transpiled_circuit = transpiler.run(transpiled_circuit)
# We group all commuting observables
# These groups are the Pauli X, Y and Z operators on individual qubits
observables_x = [
SparsePauliOp(id[:i] + "X" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_y = [
SparsePauliOp(id[:i] + "Y" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_z = [
SparsePauliOp(id[:i] + "Z" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
# We define the primitive unified blocs (PUBs) consisting of the embedding circuit,
# set of observables and the circuit parameters
pub_x = (transpiled_circuit, observables_x)
pub_y = (transpiled_circuit, observables_y)
pub_z = (transpiled_circuit, observables_z)
# We define and run the estimator to obtain <X>, <Y> and <Z> on all qubits
estimator = Estimator(options=options)
job = estimator.run([pub_x, pub_y, pub_z])
jobs_train.append(job)
Training data progress: 100%|██████████| 172/172 [13:03<00:00, 4.55s/it]
לאחר השלמת העבודות, נוכל לאחזר את התוצאות.
if run_experiment:
for i in tqdm.tqdm(
range(len(train_data)), desc="Retrieving training data results"
):
# Completed job
job = jobs_train[i]
# Job results
job_result_x = job.result()[0].data.evs
job_result_y = job.result()[1].data.evs
job_result_z = job.result()[2].data.evs
# Record <X>, <Y> and <Z> on all qubits for the current datapoint
projections_train.append([job_result_x, job_result_y, job_result_z])
נחזור על כך גם עבור מסד הנתונים לבדיקה.
# Identity operator on all qubits
id = "I" * num_qubits
# projections_test[i][j][k] will be the expectation value of the j-th Pauli operator (0: X, 1: Y, 2: Z)
# of datapoint i on qubit k
projections_test = []
jobs_test = []
# Experiment options for error mitigation
num_randomizations = 300
shots_per_randomization = 100
noise_factors = [1, 3, 5]
experimental_opts = {}
experimental_opts["resilience"] = {
"measure_mitigation": True,
"zne_mitigation": True,
"zne": {
"noise_factors": noise_factors,
"amplifier": "gate_folding",
"return_all_extrapolated": True,
"return_unextrapolated": True,
"extrapolated_noise_factors": [0] + noise_factors,
},
}
experimental_opts["twirling"] = {
"num_randomizations": num_randomizations,
"shots_per_randomization": shots_per_randomization,
"strategy": "active-accum",
}
options = EstimatorOptions(experimental=experimental_opts)
if run_experiment:
with Batch(backend=backend):
for i in tqdm.tqdm(range(len(test_data)), desc="Test data progress"):
# Get test sample
parameters = test_data[i]
# Bind parameter to the circuit and simplify it
qc_bound = qc.assign_parameters(parameters)
transpiler = generate_preset_pass_manager(
optimization_level=3, basis_gates=["u3", "cz"]
)
transpiled_circuit = transpiler.run(qc_bound)
# Transpile for hardware
transpiler = generate_preset_pass_manager(
optimization_level=3, target=target
)
transpiled_circuit = transpiler.run(transpiled_circuit)
# We group all commuting observables
# These groups are the Pauli X, Y and Z operators on individual qubits
observables_x = [
SparsePauliOp(id[:i] + "X" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_y = [
SparsePauliOp(id[:i] + "Y" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
observables_z = [
SparsePauliOp(id[:i] + "Z" + id[(i + 1) :]).apply_layout(
transpiled_circuit.layout
)
for i in range(num_qubits)
]
# We define the primitive unified blocs (PUBs) consisting of the embedding circuit,
# set of observables and the circuit parameters
pub_x = (transpiled_circuit, observables_x)
pub_y = (transpiled_circuit, observables_y)
pub_z = (transpiled_circuit, observables_z)
# We define and run the estimator to obtain <X>, <Y> and <Z> on all qubits
estimator = Estimator(options=options)
job = estimator.run([pub_x, pub_y, pub_z])
jobs_test.append(job)
Test data progress: 100%|██████████| 74/74 [00:13<00:00, 5.56it/s]
ניתן לאחזר את התוצאות כפי שעשינו קודם.
if run_experiment:
for i in tqdm.tqdm(
range(len(test_data)), desc="Retrieving test data results"
):
# Completed job
job = jobs_test[i]
# Job results
job_result_x = job.result()[0].data.evs
job_result_y = job.result()[1].data.evs
job_result_z = job.result()[2].data.evs
# Record <X>, <Y> and <Z> on all qubits for the current datapoint
projections_test.append([job_result_x, job_result_y, job_result_z])
שלב 4: עיבוד לאחר-מדידה והחזרת התוצאה בפורמט קלאסי רצוי
הגדרת הגרעין הקוונטי המוקרן
הגרעין הקוונטי המוקרן מוגדר באמצעות פונקציית הגרעין הבאה:
במשוואה לעיל, הוא היפר-פרמטר ניתן לכיוון. הכניסות הן איברי מטריצת הגרעין .
בעזרת הגדרת ה-1-RDMs ניתן לראות שהאיברים הבודדים בתוך פונקציית הגרעין ניתנים לחישוב כ-, כאשר . ערכי התוחלת הללו הם בדיוק מה שמדדנו לעיל.
בשימוש ב-scikit-learn, ניתן לחשב את הגרעין בקלות רבה אף יותר. הדבר נובע מזמינותה של פונקציית הגרעין הרדיאלית ('rbf') המוכנה לשימוש: . ראשית, עלינו לעצב מחדש את מערכי ההיטל של נתוני האימון והבדיקה לפי מערכים דו-ממדיים.
שימו לב שמעבר על כלל מערך הנתונים עשוי לארוך כ-80 דקות על ה-QPU. כדי להבטיח שיתר המדריך ניתן לביצוע בנוחות, אנחנו מספקים גם היטלים מניסוי שבוצע קודם לכן (הכלולים בקבצים שהורדתם בבלוק הקוד Download dataset). אם ביצעתם את האימון בעצמכם, תוכלו להמשיך את המדריך עם התוצאות שלכם.
if run_experiment:
projections_train = np.array(projections_train).reshape(
len(projections_train), -1
)
projections_test = np.array(projections_test).reshape(
len(projections_test), -1
)
else:
projections_train = np.loadtxt("projections_train.txt")
projections_test = np.loadtxt("projections_test.txt")
מכונת וקטורי תמיכה (SVM)
כעת ניתן להריץ SVM קלאסי על הגרעין שחושב מראש, ולהשתמש בגרעין שבין מערכי הבדיקה והאימון לצורך חיזוי.
# Range of 'C' and 'gamma' values as SVC hyperparameters
C_range = [0.001, 0.005, 0.007]
C_range.extend([x * 0.01 for x in range(1, 11)])
C_range.extend([x * 0.25 for x in range(1, 60)])
C_range.extend(
[
20,
50,
100,
200,
500,
700,
1000,
1100,
1200,
1300,
1400,
1500,
1700,
2000,
]
)
gamma_range = ["auto", "scale", 0.001, 0.005, 0.007]
gamma_range.extend([x * 0.01 for x in range(1, 11)])
gamma_range.extend([x * 0.25 for x in range(1, 60)])
gamma_range.extend([20, 50, 100])
param_grid = dict(C=C_range, gamma=gamma_range)
# Support vector classifier
svc = SVC(kernel="rbf")
# Define the cross validation
cv = StratifiedKFold(n_splits=10)
# Grid search for hyperparameter tuning (q: quantum)
grid_search_q = GridSearchCV(
svc, param_grid, cv=cv, verbose=1, n_jobs=-1, scoring="f1_weighted"
)
grid_search_q.fit(projections_train, train_labels)
# Best model with best parameters
best_svc_q = grid_search_q.best_estimator_
print(
f"The best parameters are {grid_search_q.best_params_} with a score of {grid_search_q.best_score_:.4f}"
)
# Test accuracy
accuracy_q = best_svc_q.score(projections_test, test_labels)
print(f"Test accuracy with best model: {accuracy_q:.4f}")
Fitting 10 folds for each of 6622 candidates, totalling 66220 fits
The best parameters are {'C': 8.5, 'gamma': 0.01} with a score of 0.6980
Test accuracy with best model: 0.8108
השוואה לרף קלאסי
ניתן להריץ SVM קלאסי עם פונקציית הגרעין הרדיאלית, ללא ביצוע היטל קוונטי. תוצאה זו משמשת כרף הביצועים הקלאסי שלנו.
# Support vector classifier
svc = SVC(kernel="rbf")
# Grid search for hyperparameter tuning (c: classical)
grid_search_c = GridSearchCV(
svc, param_grid, cv=cv, verbose=1, n_jobs=-1, scoring="f1_weighted"
)
grid_search_c.fit(train_data, train_labels)
# Best model with best parameters
best_svc_c = grid_search_c.best_estimator_
print(
f"The best parameters are {grid_search_c.best_params_} with a score of {grid_search_c.best_score_:.4f}"
)
# Test accuracy
accuracy_c = best_svc_c.score(test_data, test_labels)
print(f"Test accuracy with best model: {accuracy_c:.4f}")
Fitting 10 folds for each of 6622 candidates, totalling 66220 fits
The best parameters are {'C': 10.75, 'gamma': 0.04} with a score of 0.7830
Test accuracy with best model: 0.7432
נספח: אימות יתרון קוונטי פוטנציאלי של מערך הנתונים במשימות למידה
לא כל מערכי הנתונים מציעים יתרון פוטנציאלי מהשימוש ב-PQKs. קיימים חסמים תיאורטיים שניתן להשתמש בהם כבדיקה מקדימה לבחון האם מערך נתונים מסוים עשוי להפיק תועלת מ-PQKs. לכימות זאת, מחברי Power of data in quantum machine learning [2] מגדירים כמויות המכונות סיבוכיות מודל קלאסית וקוונטית, והפרדה גיאומטרית בין המודלים הקלאסי והקוונטי. כדי לצפות ליתרון קוונטי פוטנציאלי מ-PQKs, ההפרדה הגיאומטרית בין הגרעינים הקלאסי והקוונטי-המוקרן צריכה להיות בסדר גודל של בערך, כאשר הוא מספר דגימות האימון. אם תנאי זה מתקיים, נבדוק את סיבוכיות המודל. אם סיבוכיות המודל הקלאסי היא בסדר גודל של בעוד שסיבוכיות המודל הקוונטי-המוקרן קטנה באופן משמעותי מ-, ניתן לצפות ליתרון פוטנציאלי מה-PQK. ההפרדה הגיאומטרית מוגדרת כדלקמן (F19 ב-[2]):
# Gamma values used in best models above
gamma_c = grid_search_c.best_params_["gamma"]
gamma_q = grid_search_q.best_params_["gamma"]
# Regularization parameter used in the best classical model above
C_c = grid_search_c.best_params_["C"]
l_c = 1 / C_c
# Classical and quantum kernels used above
K_c = rbf_kernel(train_data, train_data, gamma=gamma_c)
K_q = rbf_kernel(projections_train, projections_train, gamma=gamma_q)
# Intermediate matrices in the equation
K_c_sqrt = sqrtm(K_c)
K_q_sqrt = sqrtm(K_q)
K_c_inv = inv(K_c + l_c * np.eye(K_c.shape[0]))
K_multiplication = (
K_q_sqrt @ K_c_sqrt @ K_c_inv @ K_c_inv @ K_c_sqrt @ K_q_sqrt
)
# Geometric separation
norm = np.linalg.norm(K_multiplication, ord=np.inf)
g_cq = np.sqrt(norm)
print(
f"Geometric separation between classical and quantum kernels is {g_cq:.4f}"
)
print(np.sqrt(len(train_data)))
Geometric separation between classical and quantum kernels is 1.5440
13.114877048604
סיבוכיות המודל מוגדרת כדלקמן (M1 ב-[2]):
# Model complexity of the classical kernel
# Number of training data
N = len(train_data)
# Predicted labels
pred_labels = best_svc_c.predict(train_data)
pred_matrix = np.outer(pred_labels, pred_labels)
# Intermediate terms
K_c_inv = inv(K_c + l_c * np.eye(K_c.shape[0]))
# First term
first_sum = np.sum((K_c_inv @ K_c_inv) * pred_matrix)
first_term = l_c * np.sqrt(first_sum / N)
# Second term
second_sum = np.sum((K_c_inv @ K_c @ K_c_inv) * pred_matrix)
second_term = np.sqrt(second_sum / N)
# Model complexity
s_c = first_term + second_term
print(f"Classical model complexity is {s_c:.4f}")
Classical model complexity is 1.3578
# Model complexity of the projected quantum kernel
# Number of training data
N = len(projections_train)
# Predicted labels
pred_labels = best_svc_q.predict(projections_train)
pred_matrix = np.outer(pred_labels, pred_labels)
# Regularization parameter used in the best classical model above
C_q = grid_search_q.best_params_["C"]
l_q = 1 / C_q
# Intermediate terms
K_q_inv = inv(K_q + l_q * np.eye(K_q.shape[0]))
# First term
first_sum = np.sum((K_q_inv @ K_q_inv) * pred_matrix)
first_term = l_q * np.sqrt(first_sum / N)
# Second term
second_sum = np.sum((K_q_inv @ K_q @ K_q_inv) * pred_matrix)
second_term = np.sqrt(second_sum / N)
# Model complexity
s_q = first_term + second_term
print(f"Quantum model complexity is {s_q:.4f}")
Quantum model complexity is 1.5806
מקורות
- Utro, Filippo, et al. "Enhanced Prediction of CAR T-Cell Cytotoxicity with Quantum-Kernel Methods." arXiv preprint arXiv:2507.22710 (2025).
- Huang, Hsin-Yuan, et al. "Power of data in quantum machine learning." Nature communications 12.1 (2021): 2631.
- Daniels, Kyle G., et al. "Decoding CAR T cell phenotype using combinatorial signaling motif libraries and machine learning." Science 378.6625 (2022): 1194-1200.